A wrapper of [openalexR::oa_fetch()] function to get the number of scientific works (and a list of doi if count_only is set to FALSE) for each taxa of a phyloseq object. Each taxa name is searched in the title and abstract of the works present in Open Alex database.
Usage
tax_oa_pq(
physeq = NULL,
taxnames = NULL,
taxonomic_rank = "currentCanonicalSimple",
count_only = FALSE,
return_raw_oa = FALSE,
add_to_phyloseq = NULL,
col_prefix = NULL,
type_works = c("article", "review", "book-chapter", "book", "letter"),
verbose = TRUE,
discard_genus_alone = taxonomic_rank == "currentCanonicalSimple",
discard_NA = TRUE,
...
)Arguments
- physeq
(optional) A phyloseq object. Either `physeq` or `taxnames` must be provided, but not both.
- taxnames
(optional) A character vector of taxonomic names.
- taxonomic_rank
(Character, default "currentCanonicalSimple") The column(s) present in the @tax_table slot of the phyloseq object. Can be a vector of two columns (e.g. c("Genus", "Species")).
- count_only
(Logical, default FALSE) If TRUE, only the number of works on a given taxa is return, leading to a faster call to `openalexR::oa_fetch()`. Note that if count_only is set to TRUE all works (including e.g. preprint and dataset) are count, leading to higher number of works than if count_only is set to FALSE (see parameter `type_works`).
- return_raw_oa
(Logical, default FALSE) If TRUE, return the raw list of publications from Open Alex for each taxa as a list of data.frame. Can be useful to filter works for example by topic or by number of citations (see section examples). If TRUE, add_to_phyloseq is set to FALSE automatically.
- add_to_phyloseq
(logical, default TRUE when physeq is provided, FALSE when taxnames is provided and FALSE if return_raw_oa is set to TRUE). If TRUE, return a new phyloseq object with new columns in the tax_table slot. Automatically set to TRUE when a phyloseq object is provided and FALSE when taxnames is provided. Cannot be TRUE if `taxnames` is provided.
- col_prefix
A character string to be added as a prefix to the new columns names added to the tax_table slot of the phyloseq object (default: NULL).
- type_works
(A list of type to select) See Open Alex [documentation](https://docs.openalex.org/api-entities/works/work-object#type). Only used if count_only is set to FALSE Default is c("article", "review", "book-chapter", "book", "letter").
- verbose
(logical, default TRUE) If TRUE, prompt some messages.
- ...
Other params to passed on [openalexR::oa_fetch()]
Value
Either a tibble (if add_to_phyloseq = FALSE) or a new phyloseq object, if add_to_phyloseq = TRUE, with 1 (`n_doi`) or 4 (`n_doi`, `list_doi`, `n_citation` and `list_keywords` if `count_only` is FALSE) new column(s) in the tax_table.
- n_doi: number of publications citing this taxa in title or abstract - list_doi: list of DOIs separate by ";" - n_citation: total number of citations for all publications citing this taxa - list_keywords: list of keywords from all publications citing this taxa
Examples
# \donttest{
data_fungi_mini_cleanNames <- gna_verifier_pq(data_fungi_mini) |>
tax_oa_pq()
#> ✔ GNA verification summary:
#> • Total taxa in phyloseq: 45
#> • Taxa submitted for verification: 37
#> • Genus-level only taxa: 2
#> • Total matches found: 25
#> • Synonyms: 2 (including 2 at genus level)
#> • Accepted names: 23 (including 21 at genus level)
#> Fetching OpenAlex ■ 0% | ETA: ?
#> ℹ Fetching OpenAlex works for taxon: Stereum ostrea
#> Fetching OpenAlex ■ 0% | ETA: ?
#> Fetching OpenAlex ■■ 4% | ETA: 2m
#> ℹ Fetching OpenAlex works for taxon: Xylodon raduloides
#> Fetching OpenAlex ■■ 4% | ETA: 2m
#> Fetching OpenAlex ■■■■ 9% | ETA: 1m
#> ℹ Fetching OpenAlex works for taxon: Stereum hirsutum
#> Fetching OpenAlex ■■■■ 9% | ETA: 1m
#> Fetching OpenAlex ■■■■■ 13% | ETA: 2m
#> ℹ Fetching OpenAlex works for taxon: Trametopsis brasiliensis
#> Fetching OpenAlex ■■■■■ 13% | ETA: 2m
#> Fetching OpenAlex ■■■■■■ 17% | ETA: 2m
#> ℹ Fetching OpenAlex works for taxon: Basidiodendron eyrei
#> Fetching OpenAlex ■■■■■■ 17% | ETA: 2m
#> Fetching OpenAlex ■■■■■■■■ 22% | ETA: 1m
#> ℹ Fetching OpenAlex works for taxon: Sistotrema oblongisporum
#> Fetching OpenAlex ■■■■■■■■ 22% | ETA: 1m
#> ℹ Fetching OpenAlex works for taxon: Fomes fomentarius
#> Fetching OpenAlex ■■■■■■■■ 22% | ETA: 1m
#> Fetching OpenAlex ■■■■■■■■■■ 30% | ETA: 2m
#> ℹ Fetching OpenAlex works for taxon: Mycena renati
#> Fetching OpenAlex ■■■■■■■■■■ 30% | ETA: 2m
#> ℹ Fetching OpenAlex works for taxon: Helicogloea pellucida
#> Fetching OpenAlex ■■■■■■■■■■ 30% | ETA: 2m
#> ℹ Fetching OpenAlex works for taxon: Radulomyces molaris
#> Fetching OpenAlex ■■■■■■■■■■ 30% | ETA: 2m
#> ℹ Fetching OpenAlex works for taxon: Elmerina caryae
#> Fetching OpenAlex ■■■■■■■■■■ 30% | ETA: 2m
#> Fetching OpenAlex ■■■■■■■■■■■■■■■ 48% | ETA: 1m
#> ℹ Fetching OpenAlex works for taxon: Phanerochaete livescens
#> Fetching OpenAlex ■■■■■■■■■■■■■■■ 48% | ETA: 1m
#> ℹ Fetching OpenAlex works for taxon: Gloeohypochnicium analogum
#> Fetching OpenAlex ■■■■■■■■■■■■■■■ 48% | ETA: 1m
#> Fetching OpenAlex ■■■■■■■■■■■■■■■■■■ 57% | ETA: 38s
#> ℹ Fetching OpenAlex works for taxon: Hyphoderma roseocremeum
#> Fetching OpenAlex ■■■■■■■■■■■■■■■■■■ 57% | ETA: 38s
#> ℹ Fetching OpenAlex works for taxon: Hyphoderma setigerum
#> Fetching OpenAlex ■■■■■■■■■■■■■■■■■■ 57% | ETA: 38s
#> ℹ Fetching OpenAlex works for taxon: Trametes versicolor
#> Fetching OpenAlex ■■■■■■■■■■■■■■■■■■ 57% | ETA: 38s
#> Fetching OpenAlex ■■■■■■■■■■■■■■■■■■■■■■ 70% | ETA: 1m
#> ℹ Fetching OpenAlex works for taxon: Peniophora versiformis
#> Fetching OpenAlex ■■■■■■■■■■■■■■■■■■■■■■ 70% | ETA: 1m
#> Fetching OpenAlex ■■■■■■■■■■■■■■■■■■■■■■■ 74% | ETA: 1m
#> ℹ Fetching OpenAlex works for taxon: Exidia glandulosa
#> Fetching OpenAlex ■■■■■■■■■■■■■■■■■■■■■■■ 74% | ETA: 1m
#> Fetching OpenAlex ■■■■■■■■■■■■■■■■■■■■■■■■ 78% | ETA: 46s
#> ℹ Fetching OpenAlex works for taxon: Peniophorella pubera
#> Fetching OpenAlex ■■■■■■■■■■■■■■■■■■■■■■■■ 78% | ETA: 46s
#> Fetching OpenAlex ■■■■■■■■■■■■■■■■■■■■■■■■■■ 83% | ETA: 35s
#> ℹ Fetching OpenAlex works for taxon: Auricularia mesenterica
#> Fetching OpenAlex ■■■■■■■■■■■■■■■■■■■■■■■■■■ 83% | ETA: 35s
#> ℹ Fetching OpenAlex works for taxon: Laetisaria buckii
#> Fetching OpenAlex ■■■■■■■■■■■■■■■■■■■■■■■■■■ 83% | ETA: 35s
#> ℹ Fetching OpenAlex works for taxon: Hericium coralloides
#> Fetching OpenAlex ■■■■■■■■■■■■■■■■■■■■■■■■■■ 83% | ETA: 35s
#> Fetching OpenAlex ■■■■■■■■■■■■■■■■■■■■■■■■■■■■■■ 96% | ETA: 8s
#> ℹ Fetching OpenAlex works for taxon: Xylodon flaviporus
#> Fetching OpenAlex ■■■■■■■■■■■■■■■■■■■■■■■■■■■■■■ 96% | ETA: 8s
#> Fetching OpenAlex ■■■■■■■■■■■■■■■■■■■■■■■■■■■■■■■ 100% | ETA: 0s
#>
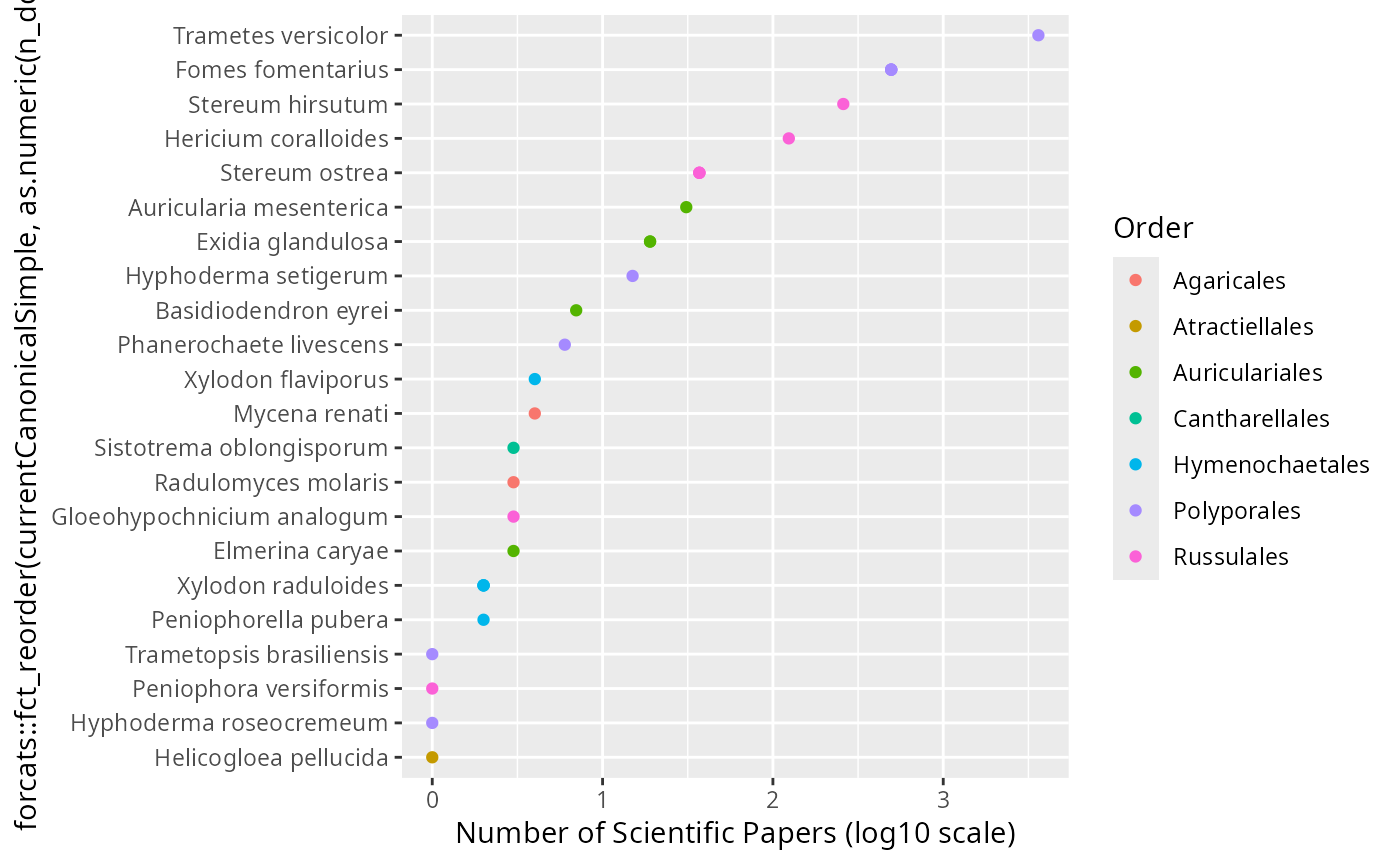
ggplot(
subset_taxa(data_fungi_mini_cleanNames, !is.na(n_doi))@tax_table,
aes(
x = log10(as.numeric(n_doi)),
y = forcats::fct_reorder(currentCanonicalSimple, as.numeric(n_doi))
)
) +
geom_point(aes(col = Order)) +
xlab("Number of Scientific Papers (log10 scale)")
 tax_oa_pq(data_fungi_mini_cleanNames, type_works = "dataset")
#> Fetching OpenAlex ■ 0% | ETA: ?
#> ℹ Fetching OpenAlex works for taxon: Stereum ostrea
#> Fetching OpenAlex ■ 0% | ETA: ?
#> ℹ Fetching OpenAlex works for taxon: Xylodon raduloides
#> Fetching OpenAlex ■ 0% | ETA: ?
#> Fetching OpenAlex ■■■■ 9% | ETA: 39s
#> ℹ Fetching OpenAlex works for taxon: Stereum hirsutum
#> Fetching OpenAlex ■■■■ 9% | ETA: 39s
#> Fetching OpenAlex ■■■■■ 13% | ETA: 1m
#> ℹ Fetching OpenAlex works for taxon: Trametopsis brasiliensis
#> Fetching OpenAlex ■■■■■ 13% | ETA: 1m
#> Fetching OpenAlex ■■■■■■ 17% | ETA: 1m
#> ℹ Fetching OpenAlex works for taxon: Basidiodendron eyrei
#> Fetching OpenAlex ■■■■■■ 17% | ETA: 1m
#> ℹ Fetching OpenAlex works for taxon: Sistotrema oblongisporum
#> Fetching OpenAlex ■■■■■■ 17% | ETA: 1m
#> Fetching OpenAlex ■■■■■■■■■ 26% | ETA: 42s
#> ℹ Fetching OpenAlex works for taxon: Fomes fomentarius
#> Fetching OpenAlex ■■■■■■■■■ 26% | ETA: 42s
#> Fetching OpenAlex ■■■■■■■■■■ 30% | ETA: 1m
#> ℹ Fetching OpenAlex works for taxon: Mycena renati
#> Fetching OpenAlex ■■■■■■■■■■ 30% | ETA: 1m
#> Fetching OpenAlex ■■■■■■■■■■■ 35% | ETA: 1m
#> ℹ Fetching OpenAlex works for taxon: Helicogloea pellucida
#> Fetching OpenAlex ■■■■■■■■■■■ 35% | ETA: 1m
#> ℹ Fetching OpenAlex works for taxon: Radulomyces molaris
#> Fetching OpenAlex ■■■■■■■■■■■ 35% | ETA: 1m
#> ℹ Fetching OpenAlex works for taxon: Elmerina caryae
#> Fetching OpenAlex ■■■■■■■■■■■ 35% | ETA: 1m
#> Fetching OpenAlex ■■■■■■■■■■■■■■■ 48% | ETA: 40s
#> ℹ Fetching OpenAlex works for taxon: Phanerochaete livescens
#> Fetching OpenAlex ■■■■■■■■■■■■■■■ 48% | ETA: 40s
#> ℹ Fetching OpenAlex works for taxon: Gloeohypochnicium analogum
#> Fetching OpenAlex ■■■■■■■■■■■■■■■ 48% | ETA: 40s
#> ℹ Fetching OpenAlex works for taxon: Hyphoderma roseocremeum
#> Fetching OpenAlex ■■■■■■■■■■■■■■■ 48% | ETA: 40s
#> Fetching OpenAlex ■■■■■■■■■■■■■■■■■■■ 61% | ETA: 26s
#> ℹ Fetching OpenAlex works for taxon: Hyphoderma setigerum
#> Fetching OpenAlex ■■■■■■■■■■■■■■■■■■■ 61% | ETA: 26s
#> ℹ Fetching OpenAlex works for taxon: Trametes versicolor
#> Fetching OpenAlex ■■■■■■■■■■■■■■■■■■■ 61% | ETA: 26s
#> Fetching OpenAlex ■■■■■■■■■■■■■■■■■■■■■■ 70% | ETA: 1m
#> ℹ Fetching OpenAlex works for taxon: Peniophora versiformis
#> Fetching OpenAlex ■■■■■■■■■■■■■■■■■■■■■■ 70% | ETA: 1m
#> ℹ Fetching OpenAlex works for taxon: Exidia glandulosa
#> Fetching OpenAlex ■■■■■■■■■■■■■■■■■■■■■■ 70% | ETA: 1m
#> Fetching OpenAlex ■■■■■■■■■■■■■■■■■■■■■■■■ 78% | ETA: 44s
#> ℹ Fetching OpenAlex works for taxon: Peniophorella pubera
#> Fetching OpenAlex ■■■■■■■■■■■■■■■■■■■■■■■■ 78% | ETA: 44s
#> ℹ Fetching OpenAlex works for taxon: Auricularia mesenterica
#> Fetching OpenAlex ■■■■■■■■■■■■■■■■■■■■■■■■ 78% | ETA: 44s
#> Fetching OpenAlex ■■■■■■■■■■■■■■■■■■■■■■■■■■■ 87% | ETA: 24s
#> ℹ Fetching OpenAlex works for taxon: Laetisaria buckii
#> Fetching OpenAlex ■■■■■■■■■■■■■■■■■■■■■■■■■■■ 87% | ETA: 24s
#> ℹ Fetching OpenAlex works for taxon: Hericium coralloides
#> Fetching OpenAlex ■■■■■■■■■■■■■■■■■■■■■■■■■■■ 87% | ETA: 24s
#> Fetching OpenAlex ■■■■■■■■■■■■■■■■■■■■■■■■■■■■■■ 96% | ETA: 8s
#> ℹ Fetching OpenAlex works for taxon: Xylodon flaviporus
#> Fetching OpenAlex ■■■■■■■■■■■■■■■■■■■■■■■■■■■■■■ 96% | ETA: 8s
#> Fetching OpenAlex ■■■■■■■■■■■■■■■■■■■■■■■■■■■■■■■ 100% | ETA: 0s
#>
#> Warning: Column names already exist in tax_table: "n_doi", "list_doi", "n_citation", and
#> "list_keywords"
#> ℹ Adding prefix 'oa_' to avoid conflicts
#> phyloseq-class experiment-level object
#> otu_table() OTU Table: [ 45 taxa and 137 samples ]
#> sample_data() Sample Data: [ 137 samples by 7 sample variables ]
#> tax_table() Taxonomy Table: [ 45 taxa by 28 taxonomic ranks ]
#> refseq() DNAStringSet: [ 45 reference sequences ]
list_pub_raw <- tax_oa_pq(data_fungi_mini_cleanNames,
col_prefix = "oa_",
return_raw_oa = TRUE
)
#> ℹ `add_to_phyloseq` is set to FALSE when `return_raw_oa` is TRUE
#> ℹ Fetching OpenAlex works for taxon: Stereum ostrea
#> ℹ Fetching OpenAlex works for taxon: Xylodon raduloides
#> ■■■■■ 13% | ETA: 24s
#> ℹ Fetching OpenAlex works for taxon: Stereum hirsutum
#> ■■■■■ 13% | ETA: 24s
#> ■■■■■■ 17% | ETA: 1m
#> ℹ Fetching OpenAlex works for taxon: Trametopsis brasiliensis
#> ■■■■■■ 17% | ETA: 1m
#> ℹ Fetching OpenAlex works for taxon: Basidiodendron eyrei
#> ■■■■■■ 17% | ETA: 1m
#> ℹ Fetching OpenAlex works for taxon: Sistotrema oblongisporum
#> ■■■■■■ 17% | ETA: 1m
#> ■■■■■■■■■■ 30% | ETA: 35s
#> ℹ Fetching OpenAlex works for taxon: Fomes fomentarius
#> ■■■■■■■■■■ 30% | ETA: 35s
#> ■■■■■■■■■■■ 35% | ETA: 1m
#> ℹ Fetching OpenAlex works for taxon: Mycena renati
#> ■■■■■■■■■■■ 35% | ETA: 1m
#> ℹ Fetching OpenAlex works for taxon: Helicogloea pellucida
#> ■■■■■■■■■■■ 35% | ETA: 1m
#> ℹ Fetching OpenAlex works for taxon: Radulomyces molaris
#> ■■■■■■■■■■■ 35% | ETA: 1m
#> ■■■■■■■■■■■■■■■ 48% | ETA: 36s
#> ℹ Fetching OpenAlex works for taxon: Elmerina caryae
#> ■■■■■■■■■■■■■■■ 48% | ETA: 36s
#> ℹ Fetching OpenAlex works for taxon: Phanerochaete livescens
#> ■■■■■■■■■■■■■■■ 48% | ETA: 36s
#> ℹ Fetching OpenAlex works for taxon: Gloeohypochnicium analogum
#> ■■■■■■■■■■■■■■■ 48% | ETA: 36s
#> ■■■■■■■■■■■■■■■■■■■ 61% | ETA: 24s
#> ℹ Fetching OpenAlex works for taxon: Hyphoderma roseocremeum
#> ■■■■■■■■■■■■■■■■■■■ 61% | ETA: 24s
#> ℹ Fetching OpenAlex works for taxon: Hyphoderma setigerum
#> ■■■■■■■■■■■■■■■■■■■ 61% | ETA: 24s
#> ■■■■■■■■■■■■■■■■■■■■■■ 70% | ETA: 17s
#> ℹ Fetching OpenAlex works for taxon: Trametes versicolor
#> ■■■■■■■■■■■■■■■■■■■■■■ 70% | ETA: 17s
#> ■■■■■■■■■■■■■■■■■■■■■■■ 74% | ETA: 1m
#> ℹ Fetching OpenAlex works for taxon: Peniophora versiformis
#> ■■■■■■■■■■■■■■■■■■■■■■■ 74% | ETA: 1m
#> ℹ Fetching OpenAlex works for taxon: Exidia glandulosa
#> ■■■■■■■■■■■■■■■■■■■■■■■ 74% | ETA: 1m
#> ■■■■■■■■■■■■■■■■■■■■■■■■■■ 83% | ETA: 31s
#> ℹ Fetching OpenAlex works for taxon: Peniophorella pubera
#> ■■■■■■■■■■■■■■■■■■■■■■■■■■ 83% | ETA: 31s
#> ℹ Fetching OpenAlex works for taxon: Auricularia mesenterica
#> ■■■■■■■■■■■■■■■■■■■■■■■■■■ 83% | ETA: 31s
#> ■■■■■■■■■■■■■■■■■■■■■■■■■■■■ 91% | ETA: 14s
#> ℹ Fetching OpenAlex works for taxon: Laetisaria buckii
#> ■■■■■■■■■■■■■■■■■■■■■■■■■■■■ 91% | ETA: 14s
#> ℹ Fetching OpenAlex works for taxon: Hericium coralloides
#> ■■■■■■■■■■■■■■■■■■■■■■■■■■■■ 91% | ETA: 14s
#> ■■■■■■■■■■■■■■■■■■■■■■■■■■■■■■■ 100% | ETA: 0s
#>
#> ℹ Fetching OpenAlex works for taxon: Xylodon flaviporus
list_pub_Health_science <- lapply(list_pub_raw, function(xx) {
if (length(xx) == 0) {
return(NULL)
} else {
filter(xx, map_lgl(topics, function(tibble_item) {
if (is.null(tibble_item) || nrow(tibble_item) == 0) {
return(FALSE)
} else {
any(grepl("Health science",
tibble_item$display_name[tibble_item$type == "domain"],
ignore.case = TRUE
))
}
}))
}
})
list_pub_Ecology <- lapply(list_pub_raw, function(xx) {
if (length(xx) == 0) {
return(NULL)
} else {
filter(xx, map_lgl(topics, function(tibble_item) {
if (is.null(tibble_item) || nrow(tibble_item) == 0) {
return(FALSE)
} else {
any(grepl("Ecology",
tibble_item$display_name[tibble_item$type == "subfield"],
ignore.case = TRUE
))
}
}))
}
})
list_pub_at_least_ten_citations <-
lapply(list_pub_raw, function(xx) {
if (length(xx) == 0) {
return(NULL)
} else {
filter(xx, cited_by_count > 10)
}
})
# }
tax_oa_pq(data_fungi_mini_cleanNames, type_works = "dataset")
#> Fetching OpenAlex ■ 0% | ETA: ?
#> ℹ Fetching OpenAlex works for taxon: Stereum ostrea
#> Fetching OpenAlex ■ 0% | ETA: ?
#> ℹ Fetching OpenAlex works for taxon: Xylodon raduloides
#> Fetching OpenAlex ■ 0% | ETA: ?
#> Fetching OpenAlex ■■■■ 9% | ETA: 39s
#> ℹ Fetching OpenAlex works for taxon: Stereum hirsutum
#> Fetching OpenAlex ■■■■ 9% | ETA: 39s
#> Fetching OpenAlex ■■■■■ 13% | ETA: 1m
#> ℹ Fetching OpenAlex works for taxon: Trametopsis brasiliensis
#> Fetching OpenAlex ■■■■■ 13% | ETA: 1m
#> Fetching OpenAlex ■■■■■■ 17% | ETA: 1m
#> ℹ Fetching OpenAlex works for taxon: Basidiodendron eyrei
#> Fetching OpenAlex ■■■■■■ 17% | ETA: 1m
#> ℹ Fetching OpenAlex works for taxon: Sistotrema oblongisporum
#> Fetching OpenAlex ■■■■■■ 17% | ETA: 1m
#> Fetching OpenAlex ■■■■■■■■■ 26% | ETA: 42s
#> ℹ Fetching OpenAlex works for taxon: Fomes fomentarius
#> Fetching OpenAlex ■■■■■■■■■ 26% | ETA: 42s
#> Fetching OpenAlex ■■■■■■■■■■ 30% | ETA: 1m
#> ℹ Fetching OpenAlex works for taxon: Mycena renati
#> Fetching OpenAlex ■■■■■■■■■■ 30% | ETA: 1m
#> Fetching OpenAlex ■■■■■■■■■■■ 35% | ETA: 1m
#> ℹ Fetching OpenAlex works for taxon: Helicogloea pellucida
#> Fetching OpenAlex ■■■■■■■■■■■ 35% | ETA: 1m
#> ℹ Fetching OpenAlex works for taxon: Radulomyces molaris
#> Fetching OpenAlex ■■■■■■■■■■■ 35% | ETA: 1m
#> ℹ Fetching OpenAlex works for taxon: Elmerina caryae
#> Fetching OpenAlex ■■■■■■■■■■■ 35% | ETA: 1m
#> Fetching OpenAlex ■■■■■■■■■■■■■■■ 48% | ETA: 40s
#> ℹ Fetching OpenAlex works for taxon: Phanerochaete livescens
#> Fetching OpenAlex ■■■■■■■■■■■■■■■ 48% | ETA: 40s
#> ℹ Fetching OpenAlex works for taxon: Gloeohypochnicium analogum
#> Fetching OpenAlex ■■■■■■■■■■■■■■■ 48% | ETA: 40s
#> ℹ Fetching OpenAlex works for taxon: Hyphoderma roseocremeum
#> Fetching OpenAlex ■■■■■■■■■■■■■■■ 48% | ETA: 40s
#> Fetching OpenAlex ■■■■■■■■■■■■■■■■■■■ 61% | ETA: 26s
#> ℹ Fetching OpenAlex works for taxon: Hyphoderma setigerum
#> Fetching OpenAlex ■■■■■■■■■■■■■■■■■■■ 61% | ETA: 26s
#> ℹ Fetching OpenAlex works for taxon: Trametes versicolor
#> Fetching OpenAlex ■■■■■■■■■■■■■■■■■■■ 61% | ETA: 26s
#> Fetching OpenAlex ■■■■■■■■■■■■■■■■■■■■■■ 70% | ETA: 1m
#> ℹ Fetching OpenAlex works for taxon: Peniophora versiformis
#> Fetching OpenAlex ■■■■■■■■■■■■■■■■■■■■■■ 70% | ETA: 1m
#> ℹ Fetching OpenAlex works for taxon: Exidia glandulosa
#> Fetching OpenAlex ■■■■■■■■■■■■■■■■■■■■■■ 70% | ETA: 1m
#> Fetching OpenAlex ■■■■■■■■■■■■■■■■■■■■■■■■ 78% | ETA: 44s
#> ℹ Fetching OpenAlex works for taxon: Peniophorella pubera
#> Fetching OpenAlex ■■■■■■■■■■■■■■■■■■■■■■■■ 78% | ETA: 44s
#> ℹ Fetching OpenAlex works for taxon: Auricularia mesenterica
#> Fetching OpenAlex ■■■■■■■■■■■■■■■■■■■■■■■■ 78% | ETA: 44s
#> Fetching OpenAlex ■■■■■■■■■■■■■■■■■■■■■■■■■■■ 87% | ETA: 24s
#> ℹ Fetching OpenAlex works for taxon: Laetisaria buckii
#> Fetching OpenAlex ■■■■■■■■■■■■■■■■■■■■■■■■■■■ 87% | ETA: 24s
#> ℹ Fetching OpenAlex works for taxon: Hericium coralloides
#> Fetching OpenAlex ■■■■■■■■■■■■■■■■■■■■■■■■■■■ 87% | ETA: 24s
#> Fetching OpenAlex ■■■■■■■■■■■■■■■■■■■■■■■■■■■■■■ 96% | ETA: 8s
#> ℹ Fetching OpenAlex works for taxon: Xylodon flaviporus
#> Fetching OpenAlex ■■■■■■■■■■■■■■■■■■■■■■■■■■■■■■ 96% | ETA: 8s
#> Fetching OpenAlex ■■■■■■■■■■■■■■■■■■■■■■■■■■■■■■■ 100% | ETA: 0s
#>
#> Warning: Column names already exist in tax_table: "n_doi", "list_doi", "n_citation", and
#> "list_keywords"
#> ℹ Adding prefix 'oa_' to avoid conflicts
#> phyloseq-class experiment-level object
#> otu_table() OTU Table: [ 45 taxa and 137 samples ]
#> sample_data() Sample Data: [ 137 samples by 7 sample variables ]
#> tax_table() Taxonomy Table: [ 45 taxa by 28 taxonomic ranks ]
#> refseq() DNAStringSet: [ 45 reference sequences ]
list_pub_raw <- tax_oa_pq(data_fungi_mini_cleanNames,
col_prefix = "oa_",
return_raw_oa = TRUE
)
#> ℹ `add_to_phyloseq` is set to FALSE when `return_raw_oa` is TRUE
#> ℹ Fetching OpenAlex works for taxon: Stereum ostrea
#> ℹ Fetching OpenAlex works for taxon: Xylodon raduloides
#> ■■■■■ 13% | ETA: 24s
#> ℹ Fetching OpenAlex works for taxon: Stereum hirsutum
#> ■■■■■ 13% | ETA: 24s
#> ■■■■■■ 17% | ETA: 1m
#> ℹ Fetching OpenAlex works for taxon: Trametopsis brasiliensis
#> ■■■■■■ 17% | ETA: 1m
#> ℹ Fetching OpenAlex works for taxon: Basidiodendron eyrei
#> ■■■■■■ 17% | ETA: 1m
#> ℹ Fetching OpenAlex works for taxon: Sistotrema oblongisporum
#> ■■■■■■ 17% | ETA: 1m
#> ■■■■■■■■■■ 30% | ETA: 35s
#> ℹ Fetching OpenAlex works for taxon: Fomes fomentarius
#> ■■■■■■■■■■ 30% | ETA: 35s
#> ■■■■■■■■■■■ 35% | ETA: 1m
#> ℹ Fetching OpenAlex works for taxon: Mycena renati
#> ■■■■■■■■■■■ 35% | ETA: 1m
#> ℹ Fetching OpenAlex works for taxon: Helicogloea pellucida
#> ■■■■■■■■■■■ 35% | ETA: 1m
#> ℹ Fetching OpenAlex works for taxon: Radulomyces molaris
#> ■■■■■■■■■■■ 35% | ETA: 1m
#> ■■■■■■■■■■■■■■■ 48% | ETA: 36s
#> ℹ Fetching OpenAlex works for taxon: Elmerina caryae
#> ■■■■■■■■■■■■■■■ 48% | ETA: 36s
#> ℹ Fetching OpenAlex works for taxon: Phanerochaete livescens
#> ■■■■■■■■■■■■■■■ 48% | ETA: 36s
#> ℹ Fetching OpenAlex works for taxon: Gloeohypochnicium analogum
#> ■■■■■■■■■■■■■■■ 48% | ETA: 36s
#> ■■■■■■■■■■■■■■■■■■■ 61% | ETA: 24s
#> ℹ Fetching OpenAlex works for taxon: Hyphoderma roseocremeum
#> ■■■■■■■■■■■■■■■■■■■ 61% | ETA: 24s
#> ℹ Fetching OpenAlex works for taxon: Hyphoderma setigerum
#> ■■■■■■■■■■■■■■■■■■■ 61% | ETA: 24s
#> ■■■■■■■■■■■■■■■■■■■■■■ 70% | ETA: 17s
#> ℹ Fetching OpenAlex works for taxon: Trametes versicolor
#> ■■■■■■■■■■■■■■■■■■■■■■ 70% | ETA: 17s
#> ■■■■■■■■■■■■■■■■■■■■■■■ 74% | ETA: 1m
#> ℹ Fetching OpenAlex works for taxon: Peniophora versiformis
#> ■■■■■■■■■■■■■■■■■■■■■■■ 74% | ETA: 1m
#> ℹ Fetching OpenAlex works for taxon: Exidia glandulosa
#> ■■■■■■■■■■■■■■■■■■■■■■■ 74% | ETA: 1m
#> ■■■■■■■■■■■■■■■■■■■■■■■■■■ 83% | ETA: 31s
#> ℹ Fetching OpenAlex works for taxon: Peniophorella pubera
#> ■■■■■■■■■■■■■■■■■■■■■■■■■■ 83% | ETA: 31s
#> ℹ Fetching OpenAlex works for taxon: Auricularia mesenterica
#> ■■■■■■■■■■■■■■■■■■■■■■■■■■ 83% | ETA: 31s
#> ■■■■■■■■■■■■■■■■■■■■■■■■■■■■ 91% | ETA: 14s
#> ℹ Fetching OpenAlex works for taxon: Laetisaria buckii
#> ■■■■■■■■■■■■■■■■■■■■■■■■■■■■ 91% | ETA: 14s
#> ℹ Fetching OpenAlex works for taxon: Hericium coralloides
#> ■■■■■■■■■■■■■■■■■■■■■■■■■■■■ 91% | ETA: 14s
#> ■■■■■■■■■■■■■■■■■■■■■■■■■■■■■■■ 100% | ETA: 0s
#>
#> ℹ Fetching OpenAlex works for taxon: Xylodon flaviporus
list_pub_Health_science <- lapply(list_pub_raw, function(xx) {
if (length(xx) == 0) {
return(NULL)
} else {
filter(xx, map_lgl(topics, function(tibble_item) {
if (is.null(tibble_item) || nrow(tibble_item) == 0) {
return(FALSE)
} else {
any(grepl("Health science",
tibble_item$display_name[tibble_item$type == "domain"],
ignore.case = TRUE
))
}
}))
}
})
list_pub_Ecology <- lapply(list_pub_raw, function(xx) {
if (length(xx) == 0) {
return(NULL)
} else {
filter(xx, map_lgl(topics, function(tibble_item) {
if (is.null(tibble_item) || nrow(tibble_item) == 0) {
return(FALSE)
} else {
any(grepl("Ecology",
tibble_item$display_name[tibble_item$type == "subfield"],
ignore.case = TRUE
))
}
}))
}
})
list_pub_at_least_ten_citations <-
lapply(list_pub_raw, function(xx) {
if (length(xx) == 0) {
return(NULL)
} else {
filter(xx, cited_by_count > 10)
}
})
# }